

2015国际代谢工程峰会圆满落幕
2015年12月2日,国际代谢工程大会(Metabolic Engineering Summit)在北京国际会议中心圆满落幕。这次会议聚集了30多名来自世界各国的顶尖科学家和工业界精英,参会者达到700多名,是中国合成生物学和代谢工程领域举办的规模最大、规格最高的国际学术会议。本次会议的主题是“‘合成生物学’时代下的生物制造”。
国际代谢工程协会(IMES)主席Jens Nielsen高度评价了本次大会,在送别晚宴上宣布本届大会圆满落幕,对会议的主办方以及志愿者表示感谢,向谭天伟院士及陈国强教授颁发感谢证书。

送别晚宴,Jens Nielsen向大会主席谭天伟院士及陈国强教授致谢
近年来,代谢工程和合成生物学研究在世界范围内发展迅猛,成为生命科学领域内发展最快的方向之一。为了更好的促进代谢工程和合成生物学在中国的发展,国际代谢工程协会(IMES)于2015年11月30日-12月2日在中国北京举办本届峰会。此次会议是IMES在中国举办的首届代谢工程峰会,在中国工程院、国际代谢工程协会、美国化学学会、亚洲生物技术联盟和世界工业生物技术委员会的共同支持下,由清华大学、北京化工大学、中科院微生物所、中国科学院-发展中国家科学院生物技术卓越中心、武汉生物技术研究院、深圳大学等多所高校和研究机构联合承办。
合成生物学和代谢工程作为生物领域内新兴的热点,在人类认识生命、揭示生命奥秘、重新设计及改造生物等方面具有重大的科学意义,合成生物学将催生下一次生物技术革命,是改变世界的10大新技术之一。我国科技部十分重视“合成生物学”研究,起步较早,2010年以来已经启动了合成生物学的9个973项目,迄今为止已经取得了很多可喜可贺的成果。这次会议的主题是“合成生物学”,符合国家“十三五”的发展战略,在习近平主席、刘延东副总理的高度重视下,“十三五”计划我国把“合成生物学”列为重大专项。

大会共同主席谭天伟院士、陈国强教授、李寅教授、蔡志明院长、张立新教授、刘天罡教授
大会第一天-欢迎晚宴
欢迎晚宴上,大会共同主席、清华大学陈国强教授主持晚宴,介绍大会背景。大会共同主席、北京化工大学谭天伟院士,大会共同主席、中科院微生物所李寅教授分别发言,表示对参会者的欢迎。
科技部基础研究司马燕合司长致词,马司长代表科技部基础研究司,对大会顺利召开表示祝贺。马燕合司长表示“当前正值国家研究制定“十三五”的科技创新发展规划,合成生物学将是生命科学和生物技术领域的重要内容之一”。最后预祝大会圆满成功。

马燕合司长致词
随后国际代谢工程协会(IMES)主席、瑞典皇家科学院院士JensNielsen介绍协会历史。
在大会组织者、清华大学邢新会教授主持下,大会创始人、美国工程院院士GregoryStephanopoulos作主题为“Transforming theChemical Industry via Biotechnology and Metabolic Engineering”的开场报告。提出“Biologybeyond Medicine. Biotechnology beyond Biofules.”的观点,预测合成生物学和代谢工程将是生物工业的巨大推动力。

Gregory Stephanopoulos作开场报告
大会第二天与第三天,在主会场一共有六个主题研讨会,特邀嘉宾分别进行了主题演讲。大会同时邀请了四家国内外知名的生物工业界代表,分享他们成功的经验,与参会者进行探讨。

8位国内外院士:邓子新院士、谭天伟院士、杨焕明院士、赵国屏院士、
Gregory Stephanopoulos、Jens Nielsen、James LIAO、SangYup LEE
大会第二天(三个主题研讨会以及海报展示环节)
12月1日,大会展开了三个主题研讨会。分别是“代谢工程生产天然产物”,“代谢工程变废为宝”,“代谢工程推进生物经济”。
在主题一“代谢工程生产天然产物”上,上海交通大学、武汉大学邓子新院士首先做了主题为“Approaching Synthetic Microbiologyto Harness the Metabolic Power for Novel and Improved Nucleoside Antibiotics”的专题报告。随后,加州大学伯克利分校John Dueber,大会共同主席、中科院微生物所张立新教授,大会共同主席、武汉大学刘天罡教授分别作报告。
在主题二“代谢工程变废为宝”上,谭天伟院士首先作主题为“From Cellulose to Chemicals via ME and SyntheticBiology”的专题报告。之后分别是下一届ME大会主席、神户大学Akihiko Kondo教授与李寅教授分别作报告。
在主题三“代谢工程推进生物经济”中,华大基因研究院杨焕明院士与韩国KASITSang Yup LEE分别作了主题为" From the HGP toSynthetic Biology "、 "Bio-based Production of Succinic Acid"的专题报告。上海交通大学冯雁教授,德国于利希核研究中心Wolfgang Wiechert教授等嘉宾分别作报告。
Poster展示环节,有来自国内外近180名博士、青年学者参与学术海报展示,会场交流气氛热烈。通过参会教授投票,最终选出12张最佳Poster,分获一二三等奖。
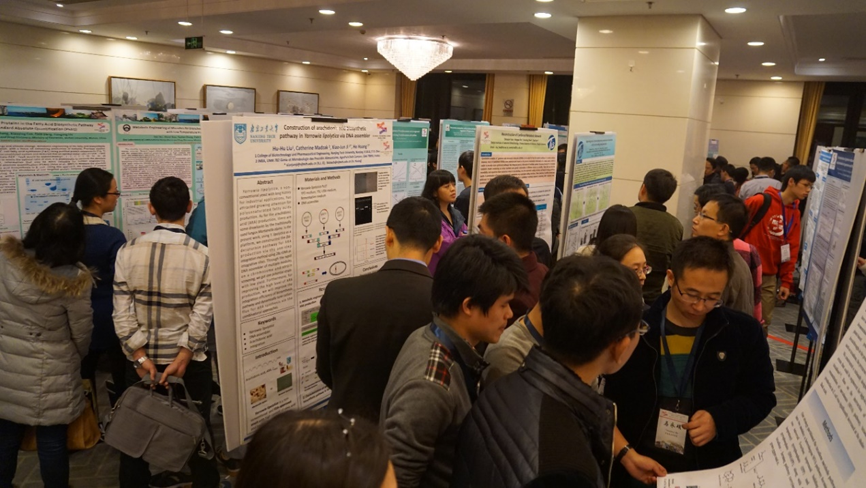
Poster展示环节,参会者相互交流
大会第三天(三个主题研讨会及送别晚宴)
12月2日,大会展开了三个主题研讨会,主题分别为“代谢工程在粮食—能源—水资源关系网中的作用”,“代谢工程作为驱动创新的促进技术”,“生物炼制在页岩气时代和降低油价中的挑战”。
在主题四“代谢工程在粮食—能源—水资源关系网中的作用”和主题五“代谢工程作为驱动创新的促进技术”中,德国明斯特大学Alexander Steinbűchel教授首先作主题为"Engineering theMetabolism of Organic Sulfur Compounds for Biosynthesis of Non-BiodegradablePolythioesters"的专题报告。之后,弗吉尼亚理工大学Yi-Heng Percival ZHANG教授等嘉宾分别做报告。
在主题六中,UCLAJames LIAO和Jens Nielsen分别作主题为"Expanding RawMaterial and Host Range for Sustainable Production of Fuels and Chemicals"、" Advancing the Design-Build-Test Cyclefor Metabolic Engineering of Yeast "的专题报告。随后,清华大学陈国强教授、杜克大学Mike Lynch教授等嘉宾分别作报告。
12月2日送别晚宴上,张立新教授和刘天罡教授的共同主持了最佳Poster颁奖仪式,谭天伟院士致闭幕词。最后,谭院士邀请所有志愿者上台,代表大会组委会表达感谢,宣布为期三天的大会画上了圆满的句号!
《人民日报》、《光明日报》、新华网、《中国经济导报》、中国青年网、凤凰网、腾讯网、搜狐网、网易等国内多家主流媒体相继报道大会。

《人民日报》、《光明日报》报道大会

全体合影
通讯员王宣,陈祥斌
2015国际代谢工程峰会圆满落幕
2015年12月2日,国际代谢工程大会(Metabolic Engineering Summit)在北京国际会议中心圆满落幕。这次会议聚集了30多名来自世界各国的顶尖科学家和工业界精英,参会者达到700多名,是中国合成生物学和代谢工程领域举办的规模最大、规格最高的国际学术会议。本次会议的主题是“‘合成生物学’时代下的生物制造”。
国际代谢工程协会(IMES)主席Jens Nielsen高度评价了本次大会,在送别晚宴上宣布本届大会圆满落幕,对会议的主办方以及志愿者表示感谢,向谭天伟院士及陈国强教授颁发感谢证书。

送别晚宴,Jens Nielsen向大会主席谭天伟院士及陈国强教授致谢
近年来,代谢工程和合成生物学研究在世界范围内发展迅猛,成为生命科学领域内发展最快的方向之一。为了更好的促进代谢工程和合成生物学在中国的发展,国际代谢工程协会(IMES)于2015年11月30日-12月2日在中国北京举办本届峰会。此次会议是IMES在中国举办的首届代谢工程峰会,在中国工程院、国际代谢工程协会、美国化学学会、亚洲生物技术联盟和世界工业生物技术委员会的共同支持下,由清华大学、北京化工大学、中科院微生物所、中国科学院-发展中国家科学院生物技术卓越中心、武汉生物技术研究院、深圳大学等多所高校和研究机构联合承办。
合成生物学和代谢工程作为生物领域内新兴的热点,在人类认识生命、揭示生命奥秘、重新设计及改造生物等方面具有重大的科学意义,合成生物学将催生下一次生物技术革命,是改变世界的10大新技术之一。我国科技部十分重视“合成生物学”研究,起步较早,2010年以来已经启动了合成生物学的9个973项目,迄今为止已经取得了很多可喜可贺的成果。这次会议的主题是“合成生物学”,符合国家“十三五”的发展战略,在习近平主席、刘延东副总理的高度重视下,“十三五”计划我国把“合成生物学”列为重大专项。

大会共同主席谭天伟院士、陈国强教授、李寅教授、蔡志明院长、张立新教授、刘天罡教授
大会第一天-欢迎晚宴
欢迎晚宴上,大会共同主席、清华大学陈国强教授主持晚宴,介绍大会背景。大会共同主席、北京化工大学谭天伟院士,大会共同主席、中科院微生物所李寅教授分别发言,表示对参会者的欢迎。
科技部基础研究司马燕合司长致词,马司长代表科技部基础研究司,对大会顺利召开表示祝贺。马燕合司长表示“当前正值国家研究制定“十三五”的科技创新发展规划,合成生物学将是生命科学和生物技术领域的重要内容之一”。最后预祝大会圆满成功。

马燕合司长致词
随后国际代谢工程协会(IMES)主席、瑞典皇家科学院院士JensNielsen介绍协会历史。
在大会组织者、清华大学邢新会教授主持下,大会创始人、美国工程院院士GregoryStephanopoulos作主题为“Transforming theChemical Industry via Biotechnology and Metabolic Engineering”的开场报告。提出“Biologybeyond Medicine. Biotechnology beyond Biofules.”的观点,预测合成生物学和代谢工程将是生物工业的巨大推动力。

Gregory Stephanopoulos作开场报告
大会第二天与第三天,在主会场一共有六个主题研讨会,特邀嘉宾分别进行了主题演讲。大会同时邀请了四家国内外知名的生物工业界代表,分享他们成功的经验,与参会者进行探讨。

8位国内外院士:邓子新院士、谭天伟院士、杨焕明院士、赵国屏院士、
Gregory Stephanopoulos、Jens Nielsen、James LIAO、SangYup LEE
大会第二天(三个主题研讨会以及海报展示环节)
12月1日,大会展开了三个主题研讨会。分别是“代谢工程生产天然产物”,“代谢工程变废为宝”,“代谢工程推进生物经济”。
在主题一“代谢工程生产天然产物”上,上海交通大学、武汉大学邓子新院士首先做了主题为“Approaching Synthetic Microbiologyto Harness the Metabolic Power for Novel and Improved Nucleoside Antibiotics”的专题报告。随后,加州大学伯克利分校John Dueber,大会共同主席、中科院微生物所张立新教授,大会共同主席、武汉大学刘天罡教授分别作报告。
在主题二“代谢工程变废为宝”上,谭天伟院士首先作主题为“From Cellulose to Chemicals via ME and SyntheticBiology”的专题报告。之后分别是下一届ME大会主席、神户大学Akihiko Kondo教授与李寅教授分别作报告。
在主题三“代谢工程推进生物经济”中,华大基因研究院杨焕明院士与韩国KASITSang Yup LEE分别作了主题为" From the HGP toSynthetic Biology "、 "Bio-based Production of Succinic Acid"的专题报告。上海交通大学冯雁教授,德国于利希核研究中心Wolfgang Wiechert教授等嘉宾分别作报告。
Poster展示环节,有来自国内外近180名博士、青年学者参与学术海报展示,会场交流气氛热烈。通过参会教授投票,最终选出12张最佳Poster,分获一二三等奖。

Poster展示环节,参会者相互交流
大会第三天(三个主题研讨会及送别晚宴)
12月2日,大会展开了三个主题研讨会,主题分别为“代谢工程在粮食—能源—水资源关系网中的作用”,“代谢工程作为驱动创新的促进技术”,“生物炼制在页岩气时代和降低油价中的挑战”。
在主题四“代谢工程在粮食—能源—水资源关系网中的作用”和主题五“代谢工程作为驱动创新的促进技术”中,德国明斯特大学Alexander Steinbűchel教授首先作主题为"Engineering theMetabolism of Organic Sulfur Compounds for Biosynthesis of Non-BiodegradablePolythioesters"的专题报告。之后,弗吉尼亚理工大学Yi-Heng Percival ZHANG教授等嘉宾分别做报告。
在主题六中,UCLAJames LIAO和Jens Nielsen分别作主题为"Expanding RawMaterial and Host Range for Sustainable Production of Fuels and Chemicals"、" Advancing the Design-Build-Test Cyclefor Metabolic Engineering of Yeast "的专题报告。随后,清华大学陈国强教授、杜克大学Mike Lynch教授等嘉宾分别作报告。
12月2日送别晚宴上,张立新教授和刘天罡教授的共同主持了最佳Poster颁奖仪式,谭天伟院士致闭幕词。最后,谭院士邀请所有志愿者上台,代表大会组委会表达感谢,宣布为期三天的大会画上了圆满的句号!
《人民日报》、《光明日报》、新华网、《中国经济导报》、中国青年网、凤凰网、腾讯网、搜狐网、网易等国内多家主流媒体相继报道大会。

《人民日报》、《光明日报》报道大会

全体合影
通讯员王宣,陈祥斌
7月16日,“清华大学合成与系统生物学研究中心成立仪式暨合成与系统生物学前沿学术研讨会”在清华大学主楼后厅举行。教育部科技司副司长雷朝滋、科技部基础司的张彦雪处长出席仪式,并对清华大学合成与系统生物学研究中心成立表示祝贺。清华大学副校长薛其坤出席仪式,并与中心顾问委员会主任王志新院士共同为中心揭牌。十余名两院院士以及来自全国各地合成生物学研究机构的嘉宾和中心共建单位的师生共两百余人出席大会。
中心主任、生命学院陈国强教授主持成立仪式。

薛其坤与王志新共同为中心揭牌。
薛其坤对清华大学合成与系统生物学研究中心的成立表示祝贺,希望中心能充分发挥清华大学优良的学科交叉传统和卓越的跨学科整合能力,形成贯穿从生物信息学处理、系统生物学建模到合成生物学理论、技术以及在工业、医学、安全等方面应用的研究链条。他表示,相信中心能推动清华的合成生物学研究迈上一个新台阶,并对我国的合成生物学研究做出重要贡献。
生命学院副院长李蓬介绍了中心成立的背景,指出合成生物学是解决粮食、环境、能源以及健康上问题的新思路。中心主任、生命学院陈国强教授全面介绍了中心的组成情况和成立的目标,中心将针对合成生物学中的关键技术和瓶颈问题展开前瞻性研究,并通过若干年的努力把中心建设成为海内外知名的合成与系统生物学中心,产生一批影响世界的工业生物技术和生物医学成果,并孕育几家在合成生物学领域有影响力的生物技术公司。
国家信息学院院院长孙家广教授、化工系副系主任邢新会教授作为部分共建单位代表发言,祝贺清华大学合成与系统生物学研究中心的成立。来自全国各地的合成生物学研究领域的兄弟单位代表先后表示祝贺,并期待与清华大学长期合作,共同提升我国在合成生物学研究领域的国际竞争力。
下午,到访的上海交通大学邓子新院士、上海交通大学冯雁教授、中科院陈润生院士和深圳第二人民医院蔡志明院长等著名专家分别作主题报告,分享合成生物学与系统生物学界最新科研成果,并与清华师生进行了交流研讨。
背景链接:
合成生物学基于工程化的思想,将天然或人工设计的生物元件模块化、标准化,并利用这些重新组装的生物学元件对生物系统进行重新设计,以实现特定的功能。2013年,麦肯锡全球研究所发布的研究报告将合成生物学评价为将改变世界的颠覆性技术。清华大学合成与系统生物学中心,包括中科院院士1名、千人计划1名、973首席4名,多名长江学者、杰青及青年千人。研究涉及高通量组学的生物信息学、复杂疾病的网络调控研究、表观基因组学及其遗传机制研究、化学品生物合成及代谢网络研究、基因线路构建及医药应用、基因合成与基因组组装、环境微生物及宏基因组学等研究领域。中心旨在发挥清华大学在生命科学和工科等方面的有利条件,以期在医学应用和工业等方面取得具有国际影响力的重要学术成果,并积极推动科研成果产业化。
供稿:生命学院 编辑:李含 蕾蕾
10月12日上午,清华大学合成与系统生物学中心-澳大利亚麦考瑞大学合作备忘录(Memorandum of Understanding)签字仪式在清华大学生物技术馆举行。麦考瑞大学常务副校长萨科·比勒陀利乌斯(Sakkie Pretorius)教授与清华大学合成与系统生物学中心张学工教授代表双方完成签字仪式。

清华大学合成与系统生物学中心-澳大利亚麦考瑞大学合作MOU签字仪式。
在签字仪式上,萨科·比勒陀利乌斯教授介绍了合成生物学的发展历史,以及麦考瑞大学的合成生物学研究情况,任轶(Ren Yi)博士介绍了清华大学与麦考瑞大学之间的博士生联合培养和交流项目。双方就合成生物学在酿酒酵母全基因组设计与合成以及合成生物学如何在农作物病虫害早期预警、防治和提升农作物产量和质量等方面的应用达成了合作意向。
相关链接:
澳大利亚麦考瑞大学:
麦考瑞大学(Macquarie University)建于1964年,其高质量的教学和科研水准受到了QS世界大学排名(QS WORLD UNIVERSITY RANKINGS)8个项目的5星认证,并且为澳洲大学学术排名前8。麦考瑞大学是澳大利亚最富进取精神的大学之一,其一直以一流的教学与创新精神著称。
清华大学合成与系统生物学中心:
清华大学合成与系统生物学中心骨干包括中科院院士1名、千人计划1名、973首席4名、长江杰青8名(人次),青年千人计划8名、优青1名、全国百篇1名。其中,主持了我国10项合成生物学973项目中的2项、以及唯一的生物信息学“973”项目。
研究涉及高通量组学的生物信息学、复杂疾病的网络调控研究、表观基因组学及其遗传机制研究、化学品生物合成及代谢网络研究、基因线路构建及医药应用、基因合成与基因组组装、环境微生物及宏基因组学等研究领域。中心在国际学术界和国内外相关产业界有较好声誉,是国内最重要的合成生物学研究队伍之一。
供稿:生命学院 学生编辑:小奇

http://me2015.csp.escience.cn/
近年来,代谢工程和合成生物学研究在中国发展迅猛,为了促进增长势头,国际代谢工程学会(IMES)决定于2015年11月30日-12月2日在北京会议中心举办代谢工程峰会。此次会议是IMES在中国举办的首届代谢工程峰会,在中国工程院、国际代谢工程学会、美国化学学会、亚洲生物技术联盟和世界工业生物技术委员会的共同支持下,由清华大学、北京化工大学、中科院微生物所、中国科学院-发展中国家科学院生物技术卓越中心、武汉生物技术研究院、深圳大学等多所高校和研究机构联合承办。
此次会议是近年来在中国举办的生命科学领域规模最大和规格最高的学术大会之一,荟萃当今全球顶尖的代谢工程专家。会议主题是“合成生物学助力可持续生物过程的发展”,各国的科学家将带来最激动人心的研究进展,来自学术界、工业界和政府的专家将共同探讨合成生物学技术如何深刻改变人类生活。
国际代谢工程大会简介
国际代谢工程大会(Metabolic Engineering Conference)是代谢工程领域最有国际影响力的会议,在同类会议中举办历史最长。从1996年MIT教授Gregory Stephanopoulos在美国举办首届会议以来,该会议每两年举办一次,旨在分享过去两年中代谢工程领域最新发展与成就,并预测未来的研究趋势。会议涵盖了系统生物学、合成生物学、生物化学工程等学科以及医疗服务、生物燃料、化学制品和新材料、微生物和哺乳动物系统等研究方向。
国际代谢工程大会历史
|
1996 美国 |
首届国际代谢工程大会前身——DNA重组生物技术会议 |
|
1998 德国 |
第二届国际代谢工程大会Metabolic Engineering II (ME II) |
|
2000 美国 |
ME III |
|
2002 意大利 |
ME IV |
|
2004 美国 |
ME V |
|
2006 荷兰 |
ME VI |
|
2008 墨西哥 |
ME VII |
|
2010 韩国 |
ME VIII |
|
2012 法国 |
ME IX |
|
2014 加拿大 |
ME X |
|
2015 中国北京 |
国际代谢工程峰会MES 2015 |
|
2016 日本 |
ME XI |
我们热忱欢迎全世界所有的朋友和同仁参会。此次峰会旨在提供以下契机:
1. 促进各国从事生物学、化学和工程学领域的科研人员在中国交流代谢工程的最新发展。
2. 促进国内外学术界、商界、媒体、政界和产业界用不同的方法和观点交流代谢工程研究和生物工业的发展。
3. 促进全球范围内将来有志从事代谢工程和合成生物学研究的博士和博士后研究人员的参与。
4. 促进国际代谢工程和合成生物学研究团队与中国科研群体之间形成系统的协作关系。
此次代谢工程峰会设立七个研讨会:
1、代谢工程生产天然产物;
2、代谢工程变废为宝;
3、代谢工程推进生物经济;
4、代谢工程在粮食—能源—水资源关系网中的作用;
5、代谢工程作为驱动创新的促进技术;
6、生物炼制在页岩气时代和降低油价中的挑战;
7、工业小组讨论;
一、时间:2015年11月30日-12月2日
二、地点:北京会议中心(地址:北京市朝阳区来广营西路88号北京会议中心大堂)
三、组织机构
支持单位:
中国工程院
国际代谢工程学会
美国化学学会
亚洲生物技术联盟
世界工业生物技术委员会
主办单位:
清华大学
北京化工大学
中国科学院-发展中国家科学院生物技术卓越中心
中国科学院微生物研究所
武汉生物技术研究院
深圳大学
四、特邀报告人名单:
Tianwei TAN (Beijing Univ Chem Technol, China), Chair
George Guo-Qiang Chen (Tsinghua Univ), Co-Chair
Yin LI (CAS, China), Co-Chair
Mark Burk (Genomatica's innovation center, USA)
Zhiming CAI (Shenzhen University, China)
Zixin DENG (Shanghai Jiao Tong University, China)
John Dueber (College of Natural Resources, UC Berkeley, USA)
Yan FENG (Shanghai Jiao Tong University, China)
Vassily Hatzimanikatis (EPFL, Switzerland)
Jeroen Hugenholtz (The Coca-Cola Company, Atlanta)
Mattheos Koffas (Rensselaer Polytechnic Institute, USA)
Akihiko Kondo (Kobe Univ, Japan)
Sang Yup Lee (KAIST, Korea)
James LIAO (Univ California, LA, USA)
Tiangang LIU (Wuhan Univ, China)
Michael D. Lynch (Duke Univ, USA)
Jens Nielsen (Chalmers Univ Technol, Sweden)
Lars Nielsen (Queensland Univ, Australia)
Philippe Soucaille(Metabilic explorer ,France)
Nigel Scrutton (Manchester Univ, UK)
Alexander Steinbüchel (Univ Munster, Germany)
Gregory Stephanopoulos (MIT, USA)
Chris Voigt (MIT, USA)
Wolfgang Wiechert (Forschungszentrum Juelich GmbH, Germany)
Yajun YAN (Univ Georgia, Athens, USA)
Sheng YANG(CAS,China)
Huanming ZHANG (Beijing genomics institute, China)
Lixin ZHANG (CAS, China)
Percival ZHANG (VirginiaTech, USA)
Xueli ZHANG (CAS, China)
Huimin ZHAO (Illinois, USA)
其中,中国院士有三名:
谭天伟院士
邓子新院士
杨焕明院士
外籍院士有四名:
Gregory Stephanopoulos (MIT, USA) 美国院士
James Liao (Univ California, LA, USA) 美国院士
Sang Yup Lee (KAIST, Korea) 韩国院士
Jens Nielsen (Chalmers Univ Technol, Sweden) 瑞典皇家院士
五、会议日程:
2015年11月30日 全天报到,大会开幕式和晚宴。
2015年12月1日 全天学术报告,工业技术小组展示和墙报展示。
2015年12月2日 全天学术报告,工业技术小组展示,最佳墙报奖颁奖和闭幕式。
六、联系方式
关于会议及注册问题欢迎邮件联系:
MES2015主席陈国强教授,+86-10-62783844,邮箱:chengq@mail.tsinghua.edu.cn
MES2015组委会清华大学博士生陈祥斌,邮箱:chenxiangbin@phalab.org
本次会议热忱欢迎代谢工程领域的专家学者、科研工作者和研究生,生物科技公司,生物医药和生物产业的风险投资人共同参与!期待与您相聚北京,共襄盛会!
2015年国际代谢工程峰会组委会
Organization Committee of MES 2015
 |
|
COLD SPRING HARBOR ASIA CONFERENCES |
|||||||||||||||||||||||||||||||
|
|
|||||||||||||||||||||||||||||||
7月16日,“清华大学合成与系统生物学研究中心成立仪式暨合成与系统生物学前沿学术研讨会”在清华大学主楼后厅举行。教育部科技司副司长雷朝滋、科技部基础司的张彦雪处长出席仪式,并对清华大学合成与系统生物学研究中心成立表示祝贺。清华大学副校长薛其坤出席仪式,并与中心顾问委员会主任王志新院士共同为中心揭牌。十余名两院院士以及来自全国各地合成生物学研究机构的嘉宾和中心共建单位的师生共两百余人出席大会。
中心主任、生命学院陈国强教授主持成立仪式。

薛其坤与王志新共同为中心揭牌。
薛其坤对清华大学合成与系统生物学研究中心的成立表示祝贺,希望中心能充分发挥清华大学优良的学科交叉传统和卓越的跨学科整合能力,形成贯穿从生物信息学处理、系统生物学建模到合成生物学理论、技术以及在工业、医学、安全等方面应用的研究链条。他表示,相信中心能推动清华的合成生物学研究迈上一个新台阶,并对我国的合成生物学研究做出重要贡献。
生命学院副院长李蓬介绍了中心成立的背景,指出合成生物学是解决粮食、环境、能源以及健康上问题的新思路。中心主任、生命学院陈国强教授全面介绍了中心的组成情况和成立的目标,中心将针对合成生物学中的关键技术和瓶颈问题展开前瞻性研究,并通过若干年的努力把中心建设成为海内外知名的合成与系统生物学中心,产生一批影响世界的工业生物技术和生物医学成果,并孕育几家在合成生物学领域有影响力的生物技术公司。
国家信息学院院院长孙家广教授、化工系副系主任邢新会教授作为部分共建单位代表发言,祝贺清华大学合成与系统生物学研究中心的成立。来自全国各地的合成生物学研究领域的兄弟单位代表先后表示祝贺,并期待与清华大学长期合作,共同提升我国在合成生物学研究领域的国际竞争力。
下午,到访的上海交通大学邓子新院士、上海交通大学冯雁教授、中科院陈润生院士和深圳第二人民医院蔡志明院长等著名专家分别作主题报告,分享合成生物学与系统生物学界最新科研成果,并与清华师生进行了交流研讨。
背景链接:
合成生物学基于工程化的思想,将天然或人工设计的生物元件模块化、标准化,并利用这些重新组装的生物学元件对生物系统进行重新设计,以实现特定的功能。2013年,麦肯锡全球研究所发布的研究报告将合成生物学评价为将改变世界的颠覆性技术。清华大学合成与系统生物学中心,包括中科院院士1名、973首席4名,多名长江学者、杰青等。研究涉及高通量组学的生物信息学、复杂疾病的网络调控研究、表观基因组学及其遗传机制研究、化学品生物合成及代谢网络研究、基因线路构建及医药应用、基因合成与基因组组装、环境微生物及宏基因组学等研究领域。中心旨在发挥清华大学在生命科学和工科等方面的有利条件,以期在医学应用和工业等方面取得具有国际影响力的重要学术成果,并积极推动科研成果产业化。
供稿:生命学院 编辑:李含 蕾蕾

http://me2015.csp.escience.cn/
近年来,代谢工程和合成生物学研究在中国发展迅猛,为了促进增长势头,国际代谢工程学会(IMES)决定于2015年11月30日-12月2日在北京会议中心举办代谢工程峰会。此次会议是IMES在中国举办的首届代谢工程峰会,在中国工程院、国际代谢工程学会、美国化学学会、亚洲生物技术联盟和世界工业生物技术委员会的共同支持下,由清华大学、北京化工大学、中科院微生物所、中国科学院-发展中国家科学院生物技术卓越中心、武汉生物技术研究院、深圳大学等多所高校和研究机构联合承办。
此次会议是近年来在中国举办的生命科学领域规模最大和规格最高的学术大会之一,荟萃当今全球顶尖的代谢工程专家。会议主题是“合成生物学助力可持续生物过程的发展”,各国的科学家将带来最激动人心的研究进展,来自学术界、工业界和政府的专家将共同探讨合成生物学技术如何深刻改变人类生活。
国际代谢工程大会简介
国际代谢工程大会(Metabolic Engineering Conference)是代谢工程领域最有国际影响力的会议,在同类会议中举办历史最长。从1996年MIT教授Gregory Stephanopoulos在美国举办首届会议以来,该会议每两年举办一次,旨在分享过去两年中代谢工程领域最新发展与成就,并预测未来的研究趋势。会议涵盖了系统生物学、合成生物学、生物化学工程等学科以及医疗服务、生物燃料、化学制品和新材料、微生物和哺乳动物系统等研究方向。
国际代谢工程大会历史
|
1996 美国 |
首届国际代谢工程大会前身——DNA重组生物技术会议 |
|
1998 德国 |
第二届国际代谢工程大会Metabolic Engineering II (ME II) |
|
2000 美国 |
ME III |
|
2002 意大利 |
ME IV |
|
2004 美国 |
ME V |
|
2006 荷兰 |
ME VI |
|
2008 墨西哥 |
ME VII |
|
2010 韩国 |
ME VIII |
|
2012 法国 |
ME IX |
|
2014 加拿大 |
ME X |
|
2015 中国北京 |
国际代谢工程峰会MES 2015 |
|
2016 日本 |
ME XI |
我们热忱欢迎全世界所有的朋友和同仁参会。此次峰会旨在提供以下契机:
1. 促进各国从事生物学、化学和工程学领域的科研人员在中国交流代谢工程的最新发展。
2. 促进国内外学术界、商界、媒体、政界和产业界用不同的方法和观点交流代谢工程研究和生物工业的发展。
3. 促进全球范围内将来有志从事代谢工程和合成生物学研究的博士和博士后研究人员的参与。
4. 促进国际代谢工程和合成生物学研究团队与中国科研群体之间形成系统的协作关系。
此次代谢工程峰会设立七个研讨会:
1、代谢工程生产天然产物;
2、代谢工程变废为宝;
3、代谢工程推进生物经济;
4、代谢工程在粮食—能源—水资源关系网中的作用;
5、代谢工程作为驱动创新的促进技术;
6、生物炼制在页岩气时代和降低油价中的挑战;
7、工业小组讨论;
一、时间:2015年11月30日-12月2日
二、地点:北京会议中心(地址:北京市朝阳区来广营西路88号北京会议中心大堂)
三、组织机构
支持单位:
中国工程院
国际代谢工程学会
美国化学学会
亚洲生物技术联盟
世界工业生物技术委员会
主办单位:
清华大学
北京化工大学
中国科学院-发展中国家科学院生物技术卓越中心
中国科学院微生物研究所
武汉生物技术研究院
深圳大学
四、特邀报告人名单:
Tianwei TAN (Beijing Univ Chem Technol, China), Chair
George Guo-Qiang Chen (Tsinghua Univ), Co-Chair
Yin LI (CAS, China), Co-Chair
Mark Burk (Genomatica's innovation center, USA)
Zhiming CAI (Shenzhen University, China)
Zixin DENG (Shanghai Jiao Tong University, China)
John Dueber (College of Natural Resources, UC Berkeley, USA)
Yan FENG (Shanghai Jiao Tong University, China)
Vassily Hatzimanikatis (EPFL, Switzerland)
Jeroen Hugenholtz (The Coca-Cola Company, Atlanta)
Mattheos Koffas (Rensselaer Polytechnic Institute, USA)
Akihiko Kondo (Kobe Univ, Japan)
Sang Yup Lee (KAIST, Korea)
James LIAO (Univ California, LA, USA)
Tiangang LIU (Wuhan Univ, China)
Michael D. Lynch (Duke Univ, USA)
Jens Nielsen (Chalmers Univ Technol, Sweden)
Lars Nielsen (Queensland Univ, Australia)
Philippe Soucaille(Metabilic explorer ,France)
Nigel Scrutton (Manchester Univ, UK)
Alexander Steinbüchel (Univ Munster, Germany)
Gregory Stephanopoulos (MIT, USA)
Chris Voigt (MIT, USA)
Wolfgang Wiechert (Forschungszentrum Juelich GmbH, Germany)
Yajun YAN (Univ Georgia, Athens, USA)
Sheng YANG(CAS,China)
Huanming ZHANG (Beijing genomics institute, China)
Lixin ZHANG (CAS, China)
Percival ZHANG (VirginiaTech, USA)
Xueli ZHANG (CAS, China)
Huimin ZHAO (Illinois, USA)
其中,中国院士有三名:
谭天伟院士
邓子新院士
杨焕明院士
外籍院士有四名:
Gregory Stephanopoulos (MIT, USA) 美国院士
James Liao (Univ California, LA, USA) 美国院士
Sang Yup Lee (KAIST, Korea) 韩国院士
Jens Nielsen (Chalmers Univ Technol, Sweden) 瑞典皇家院士
五、会议日程:
2015年11月30日 全天报到,大会开幕式和晚宴。
2015年12月1日 全天学术报告,工业技术小组展示和墙报展示。
2015年12月2日 全天学术报告,工业技术小组展示,最佳墙报奖颁奖和闭幕式。
六、联系方式
关于会议及注册问题欢迎邮件联系:
MES2015主席陈国强教授,+86-10-62783844,邮箱:chengq@mail.tsinghua.edu.cn
MES2015组委会清华大学博士生陈祥斌,邮箱:chenxiangbin@phalab.org
本次会议热忱欢迎代谢工程领域的专家学者、科研工作者和研究生,生物科技公司,生物医药和生物产业的风险投资人共同参与!期待与您相聚北京,共襄盛会!
2015年国际代谢工程峰会组委会
Organization Committee of MES 2015

http://me2015.csp.escience.cn/
近年来,代谢工程和合成生物学研究在中国发展迅猛,为了促进增长势头,国际代谢工程学会(IMES)决定于2015年11月30日-12月2日在北京会议中心举办代谢工程峰会。此次会议是IMES在中国举办的首届代谢工程峰会,在中国工程院、国际代谢工程学会、美国化学学会、亚洲生物技术联盟和世界工业生物技术委员会的共同支持下,由清华大学、北京化工大学、中科院微生物所、中国科学院-发展中国家科学院生物技术卓越中心、武汉生物技术研究院、深圳大学等多所高校和研究机构联合承办。
此次会议是近年来在中国举办的生命科学领域规模最大和规格最高的学术大会之一,荟萃当今全球顶尖的代谢工程专家。会议主题是“合成生物学助力可持续生物过程的发展”,各国的科学家将带来最激动人心的研究进展,来自学术界、工业界和政府的专家将共同探讨合成生物学技术如何深刻改变人类生活。
国际代谢工程大会简介
国际代谢工程大会(Metabolic Engineering Conference)是代谢工程领域最有国际影响力的会议,在同类会议中举办历史最长。从1996年MIT教授Gregory Stephanopoulos在美国举办首届会议以来,该会议每两年举办一次,旨在分享过去两年中代谢工程领域最新发展与成就,并预测未来的研究趋势。会议涵盖了系统生物学、合成生物学、生物化学工程等学科以及医疗服务、生物燃料、化学制品和新材料、微生物和哺乳动物系统等研究方向。
国际代谢工程大会历史
|
1996 美国 |
首届国际代谢工程大会前身——DNA重组生物技术会议 |
|
1998 德国 |
第二届国际代谢工程大会Metabolic Engineering II (ME II) |
|
2000 美国 |
ME III |
|
2002 意大利 |
ME IV |
|
2004 美国 |
ME V |
|
2006 荷兰 |
ME VI |
|
2008 墨西哥 |
ME VII |
|
2010 韩国 |
ME VIII |
|
2012 法国 |
ME IX |
|
2014 加拿大 |
ME X |
|
2015 中国北京 |
国际代谢工程峰会MES 2015 |
|
2016 日本 |
ME XI |
我们热忱欢迎全世界所有的朋友和同仁参会。此次峰会旨在提供以下契机:
1. 促进各国从事生物学、化学和工程学领域的科研人员在中国交流代谢工程的最新发展。
2. 促进国内外学术界、商界、媒体、政界和产业界用不同的方法和观点交流代谢工程研究和生物工业的发展。
3. 促进全球范围内将来有志从事代谢工程和合成生物学研究的博士和博士后研究人员的参与。
4. 促进国际代谢工程和合成生物学研究团队与中国科研群体之间形成系统的协作关系。
此次代谢工程峰会设立七个研讨会:
1、代谢工程生产天然产物;
2、代谢工程变废为宝;
3、代谢工程推进生物经济;
4、代谢工程在粮食—能源—水资源关系网中的作用;
5、代谢工程作为驱动创新的促进技术;
6、生物炼制在页岩气时代和降低油价中的挑战;
7、工业小组讨论;
一、时间:2015年11月30日-12月2日
二、地点:北京会议中心(地址:北京市朝阳区来广营西路88号北京会议中心大堂)
三、组织机构
支持单位:
中国工程院
国际代谢工程学会
美国化学学会
亚洲生物技术联盟
世界工业生物技术委员会
主办单位:
清华大学
北京化工大学
中国科学院-发展中国家科学院生物技术卓越中心
中国科学院微生物研究所
武汉生物技术研究院
深圳大学
四、特邀报告人名单:
Tianwei TAN (Beijing Univ Chem Technol, China), Chair
George Guo-Qiang Chen (Tsinghua Univ), Co-Chair
Yin LI (CAS, China), Co-Chair
Mark Burk (Genomatica's innovation center, USA)
Zhiming CAI (Shenzhen University, China)
Zixin DENG (Shanghai Jiao Tong University, China)
John Dueber (College of Natural Resources, UC Berkeley, USA)
Yan FENG (Shanghai Jiao Tong University, China)
Vassily Hatzimanikatis (EPFL, Switzerland)
Jeroen Hugenholtz (The Coca-Cola Company, Atlanta)
Mattheos Koffas (Rensselaer Polytechnic Institute, USA)
Akihiko Kondo (Kobe Univ, Japan)
Sang Yup Lee (KAIST, Korea)
James LIAO (Univ California, LA, USA)
Tiangang LIU (Wuhan Univ, China)
Michael D. Lynch (Duke Univ, USA)
Jens Nielsen (Chalmers Univ Technol, Sweden)
Lars Nielsen (Queensland Univ, Australia)
Philippe Soucaille(Metabilic explorer ,France)
Nigel Scrutton (Manchester Univ, UK)
Alexander Steinbüchel (Univ Munster, Germany)
Gregory Stephanopoulos (MIT, USA)
Chris Voigt (MIT, USA)
Wolfgang Wiechert (Forschungszentrum Juelich GmbH, Germany)
Yajun YAN (Univ Georgia, Athens, USA)
Sheng YANG(CAS,China)
Huanming ZHANG (Beijing genomics institute, China)
Lixin ZHANG (CAS, China)
Percival ZHANG (VirginiaTech, USA)
Xueli ZHANG (CAS, China)
Huimin ZHAO (Illinois, USA)
其中,中国院士有三名:
谭天伟院士
邓子新院士
杨焕明院士
外籍院士有四名:
Gregory Stephanopoulos (MIT, USA) 美国院士
James Liao (Univ California, LA, USA) 美国院士
Sang Yup Lee (KAIST, Korea) 韩国院士
Jens Nielsen (Chalmers Univ Technol, Sweden) 瑞典皇家院士
五、会议日程:
2015年11月30日 全天报到,大会开幕式和晚宴。
2015年12月1日 全天学术报告,工业技术小组展示和墙报展示。
2015年12月2日 全天学术报告,工业技术小组展示,最佳墙报奖颁奖和闭幕式。
六、联系方式
关于会议及注册问题欢迎邮件联系:
MES2015主席陈国强教授,+86-10-62783844,邮箱:chengq@mail.tsinghua.edu.cn
MES2015组委会清华大学博士生陈祥斌,邮箱:chenxiangbin@phalab.org
本次会议热忱欢迎代谢工程领域的专家学者、科研工作者和研究生,生物科技公司,生物医药和生物产业的风险投资人共同参与!期待与您相聚北京,共襄盛会!
2015年国际代谢工程峰会组委会
Organization Committee of MES 2015

图示:BIGS的流程示意图